NewtCap "Lab Science", Publicatie Alert!
NewtCap "Lab Science" - Publication Alert
30 apr, 2026
[English summary below]
De afgelopen tijd zijn er meerdere wetenschappelijke artikelen verschenen over onze Leidse
watersalamanderstudies. Graag neem ik je gaandeweg mee langs elk van deze publicaties met een korte uitleg – zodat jij weer helemaal op de hoogte bent van het laatste nieuws uit amfibieënland!
Één van de zaken waar ik aan gewerkt heb voor mijn proefschrift bij het Wielstra lab, betrof het uittesten van bepaalde labprotocollen op het DNA van verschillende soorten salamanders. Het bestuderen van het DNA van salamanders is namelijk nogal een klus, omdat deze dieren superrommelige en lange genetische codes bezitten. Véél complexer dan die van mensen en andere, meer 'simpele' wezens waar meer kennis en tools voor bestaan.
Daarom moest onze groep als het ware een 'eigen wiel' uitvinden. Zo'n wiel vervolgens verder uittesten is natuurlijk handig, om te zien hoe accuraat het werkt bij andere salamanders dan alleen de paar soorten waar ons team zich in eerste instantie op focuste. Want door zo'n methode breder te valideren, zorg je ervoor dat ook andere wetenschappers het kunnen gebruiken – en dus niet op hun beurt wéér eigen wielen hoeven uit te vinden.
[tekst gaat verder na de foto]

Aan het werk in het laboratorium van Naturalis Biodiversity Center. Het is erg bijzonder om het DNA van al die coole soorten salamanders in handen te hebben! Het is een eer om bij te kunnen dragen aan kennisvergaring voor soortgroepen die – juist door hun complexiteit, wat een uitdaging is – in de wetenschap pas later 'aan de beurt' zijn. Bron screenshot: KNAW YouTube video.
De ene salamandersoort is genetisch gezien de andere niet. Net zoals het DNA van een mens best kan verschillen van dat van andere primaten, zoals gorilla's of lemuren, geldt ditzelfde voor salamanders (nog veel sterker, eigenlijk – omdat de evolutionaire afsplitsingen daar veel verder terug de tijd in gaan). Daarom is het des te belangrijker om te kijken of een nieuwe methode een 'one size fits all'-label verdient, of dat deze juist per soort heel anders uitpakt.
De methode die wij optimaliseerden noemden wij 'NewtCap'.
Newt betekent letterlijk 'watersalamander' in het Engels, en
Cap
staat voor 'Capture', oftewel vangen. Want wat deze methode eigenlijk doet, is – in plaats van die ellendelange, rommelige DNA-streng in zijn geheel uit te lezen – eerst stukjes DNA uit een monster onttrekken (oftewel, 'vangen'), zodat die vervolgens eerst nader onderzocht kunnen worden.
Zie het als het doorspitten van een gigantisch dik boek: in plaats van het boek van A tot Z te lezen – wat enorm veel energie en tijd (en, in een zakelijke context, dus ook geld) zou kosten – scheur je uit ieder hoofdstuk één bladzijde en lees je die eerst nauwkeurig. Je zult niet direct het volledige verhaal kennen, maar je kunt wél een duidelijk overzicht krijgen van waar het boek over gaat – en van meerdere belangrijke details uit die stukken tekst! [tekst gaat verder na de foto]

Deze goudstreepsalamander (Chioglossa lusitanica) komt van nature voor in Spanje en Portugal. Hij heeft een 'gouden' rug, zoals de naam doet vermoeden, en die kleur loopt vaak door tot over de zeer lange staart. Zoals op deze foto is het gouden patroon soms ook meer roodachtig van kleur. Ik heb er nog nooit één gezien (hopelijk ooit!), maar ik heb dus wél mooi het DNA van deze coole dieren onderzocht.
Alleen: het onvoorspelbare in mijn onderzoek was dat deze lab-methode oorspronkelijk ontwikkeld was voor een zeer specifieke groep salamanders, namelijk de kam- en marmersalamanders: soorten waar ons team veel onderzoek naar doet in verband met gekke mutaties (daarover
hier meer). Na een extra optimalisatie van het lab-proces door collega Dr. James France, was het dus aan mij om de methode breder uit te testen. Om te ontdekken: hoe goed werkt het voor andere soorten?
*** Tromgeroffel... ***
Hoera!
De methode bleek, tot onze aangename verrassing, erg goed te werken bij alle watersalamanders! Dit gold voor soorten nauw verwant aan de oorspronkelijke doelsoorten, zoals de kleine watersalamander - maar ook voor veel minder verwante soorten, zoals bijvoorbeeld de ribbensalamander. Sterker nog: de methode werkte óók goed bij sommige nog veel minder verwante soorten, zoals enkele landsalamanders. Bijvoorbeeld de vuursalamander en de goudstreepsalamander (die laatste is te zien op de foto hierboven).
De resultaten van onze tests verschenen afgelopen jaar in het wetenschappelijke tijdschrift
Ecology & Evolution. Door een evolutionaire boom te bouwen (de figuur hieronder) konden we bevestigen dat de DNA-data, die bestaan uit duizenden stukjes genetische code – oftewel die 'duizenden bladzijden' die we dus uit het 'zeer dikke, hypothetische boek' scheurden – erg nuttig en nauwkeurig waren om evolutionaire vraagstukken mee op te lossen.
[tekst gaat verder na de figuur]
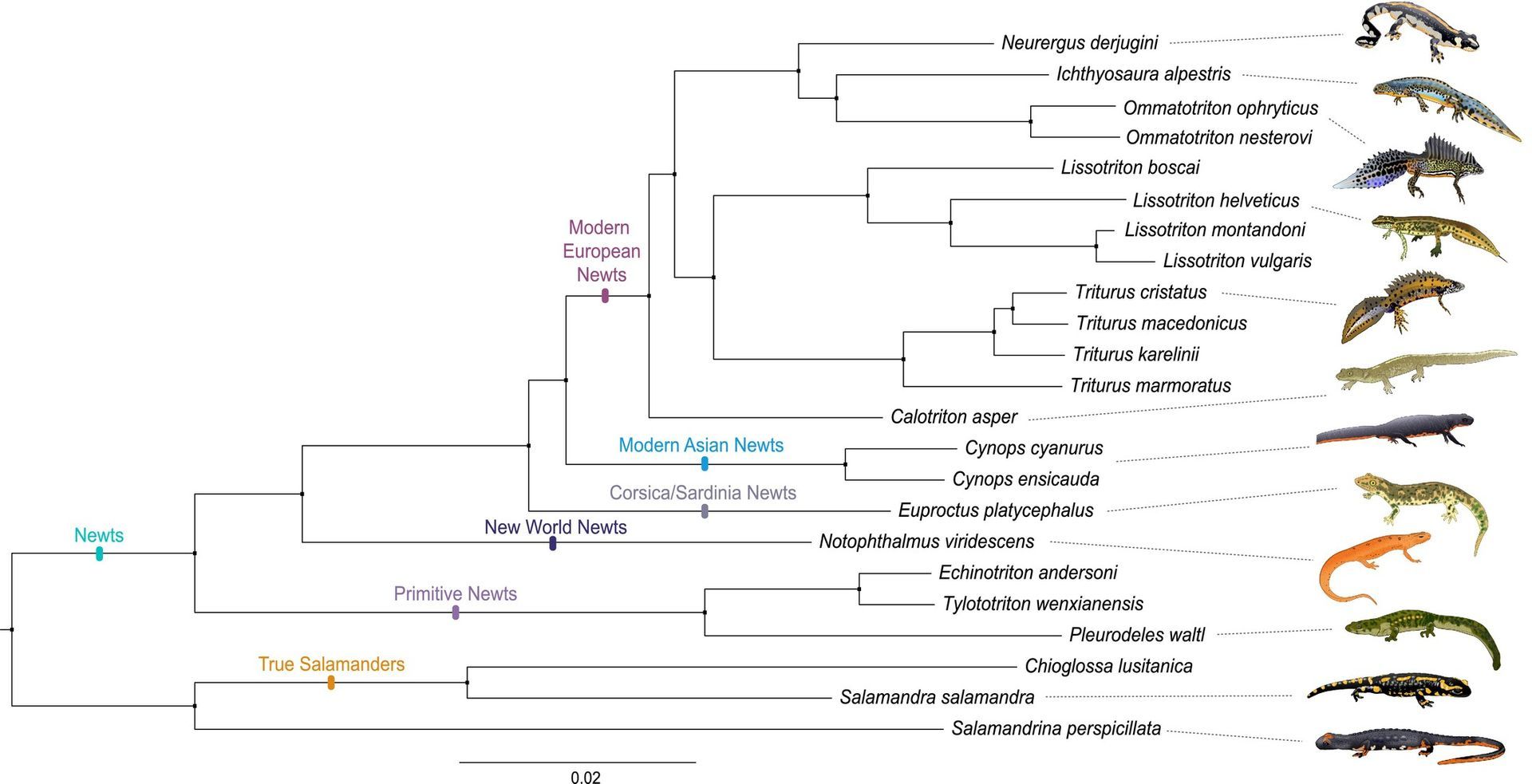
De evolutionaire stamboom van soorten binnen de zogenaamde 'Salamandridae' familie, een groep met watersalamanders als de kamsalamander (Triturus groep) en landsalamanders als de vuursalamander (Salamandra salamandra) toe behoren. Deze boom, waarin de soorten met hun Latijnse naam zijn opgenomen, bouwde ik aan de hand van de genetische data die voortvloeien uit de NewtCap methode. De boom bevestigt het verwantschapspatroon binnen de groep, die in totaal uit meer dan 100 soorten bestaat! (Bron: De Visser et al., 2025)
Los van onderzoeken of de data geschikt waren om miljoenen jaren mee terug te gaan in de tijd (want dat doe je dus eigenlijk als je zo'n boom bouwt), deden we ook analyses om na te gaan of de data binnen bepaalde groepen gebruikt kunnen worden voor vraagstukken waarbij je juist minder ver het verleden in wilt gaan. Waarbij je dus inzicht wilt krijgen in hoe soorten zich in recente periodes genetisch hebben ontwikkeld.
Ook die tests bleken zeer succesvol! Zo werkten we bijvoorbeeld samen met wetenschappers van de Universiteit van Californië in Los Angeles om te duiken in het DNA van verschillende soorten West-Amerikaanse watersalamanders – die zeer nauw verwant zijn aan elkaar, en dus heel erg op elkaar lijken, maar die juist weer níet nauw verwant zijn aan de oorspronkelijke doelsoorten van de methode. Toch bleek de methode meer dan goed genoeg om ook deze soorten duidelijk van elkaar te onderscheiden.
Verder bleek de data die NewtCap aanleverde handig om hybriden te bestuderen. Dit testten we met het DNA van kleine watersalamandersoorten uit Polen en Roemenië. Die twee soorten zijn in een kweekfaciliteit bij de Jagiellonische Universiteit in Krakau met elkaar gekruist, en sommige nakomelingen daarvan ook weer onderling. Met de juiste data kun je nagaan hoeveel vermenging er in het DNA van zulke nakomelingen zit. NewtCap bleek ook hiervoor erg handig, om dit uiteindelijk nauwkeurig te berekenen.
[tekst gaat verder na de foto]

In de Nederlandse bossen tijdens veldwerk. De watersalamanders plaatsen we kort in een cuvet om ze te bekijken – en soms nemen we wat slijm af voor DNA – voordat we ze weer gauw terugplaatsen in hun favoriete slootjes en vijvers!
Tot slot bleek de methode óók nog eens handig in het kader van natuurbescherming en monitoring binnen één en dezelfde soort. Zo testten we, in samenwerking met een hobby-kweker uit Duitsland, of we met DNA gegevens van verschillende, wilde populaties van de Bulgaarse kamsalamander (Triturus ivanbureschi) dieren in gevangenschap werden gehouden konden 'matchen' met hun wilde, geografische herkomst. Ook dit lukte!
Kortom: NewtCap is een nuttige methode om het DNA van verschillende soorten water- en landsalamanders onder de loep te nemen. Iets wat hiervoor nog niet goed mogelijk, of in ieder geval getest, was. De wetenschappelijke publicatie staat inmiddels zo'n acht maanden online en is sindsdien al meer dan duizend (!) keer geraadpleegd. Hopelijk zijn andere salamanderwetenschappers die op zoek zijn naar lab-technieken met de methode gebaat!
Ook nieuwsgierig naar de wetenschap hierachter? Dan kun je het artikel lezen via de knop hieronder:
English summary:
In this blog, I describe one of the scientific projects from my PhD at the
Wielstra lab, in which I helped test an investigative, genetic tool that we called “NewtCap” on the DNA of different salamander species. The genetic codes of salamanders are, inconveniently, extremely large and complex - making them difficult to study with methods that focus on the entirety of the genome.
Our method NewtCap solves this issue by 'capturing' selected fragments of DNA, instead of sequencing whole genomes. In the study that presents NewtCap, I specifically tested how well this method works across a wide range of species (and not just the target species from the genus Triturus, for which the tool originally was developed). We tested the tool on DNA of closely related newts, as well as way more distantly related salamanders. The results showed that the method is fairly robust and works surprisingly well across many groups, making it useful for evolutionary studies in salamanders belonging to the Salamandridae family. NewtCap allows scientists to reconstruct evolutionary relationships, distinguish closely related species, and even detect hybridization among species. In addition, the method proved valuable for conservation genetics purposes, such as tracing the geographic origin of captive individuals.
Overall, NewtCap provides an efficient and versatile tool for studying salamander DNA, opening new possibilities for research in evolution and conservation biology! You can find and read the scientific paper, published in the journal
Ecology & Evolution, via the green button above.